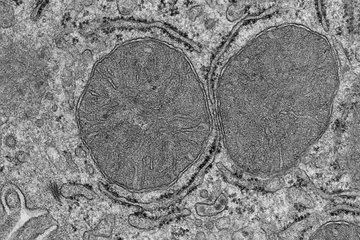
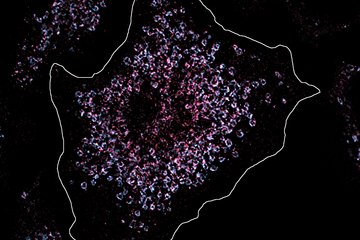
3D-Modell der Leber verbessert Diagnose
Dresdner Forscher entwickeln Lebermodelle für Diagnose von nichtalkoholischer Fettlebererkrankung
Die nicht-alkoholische Fettlebererkrankung ist in den Industrieländern eine der häufigsten chronischen Lebererkrankungen. Die histologische Analyse des Lebergewebes ist die einzige anerkannte Methode zur Diagnose und Abgrenzung verschiedener Stadien der Erkrankung. Die herkömmliche Histologie liefert jedoch nur zweidimensionale Bilder des Lebergewebes in niedriger Auflösung und vernachlässigt potenziell wichtige dreidimensionale strukturelle Veränderungen. Forscher des Max-Planck-Instituts für molekulare Zellbiologie und Genetik in Dresden und des Universitätsklinikums Carl Gustav Carus Dresden haben nun zusammen mit Kollegen der Technischen Universität Dresden dreidimensionale geometrische und funktionelle Modelle des menschlichen Lebergewebes für verschiedene Stadien der Erkrankung erstellt, die neue krankheitsbedingte Gewebeveränderungen sichtbar machen.
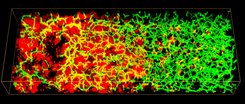
Die nicht-alkoholische Fettlebererkrankung ist durch die Anhäufung von Fett in der Leber in Verbindung mit einer Insulinresistenz gekennzeichnet, die nicht auf Alkoholkonsum zurückzuführen ist. Die Erkrankung umfasst ein Spektrum von Lebererkrankungen, von einfacher Steatose („nicht-progressiv“ und reversibel) bis hin zu nicht-alkoholischer Steatohepatitis, die zu Zirrhose, Leberkrebs oder Leberversagen führen kann und letztendlich eine Transplantation erfordert. Eine nicht-alkoholische Fettlebererkrankung ist die häufigste Ursache chronischer Lebererkrankungen. Im Jahr 2017 waren schätzungsweise 24 Prozent der Weltbevölkerung von dieser Erkrankung betroffen.
Die klassische histologische Analyse von Lebergewebe ist der Goldstandard zur Diagnose des Krankheitsverlaufes, hat aber mehrere Nachteile: Die niedrig aufgelösten 2D-Bilder des Lebergewebes ermöglichen nur eine semi-quantitative Auswertung, welche hängt von den Fähigkeiten des untersuchenden Arztes abhängt und damit sehr subjektiv sein kann. Vor allem liefern solche Bilder keine 3D-Informationen über Gewebestruktur und -funktion, denn die Leber hat eine komplexe dreidimensionale Gewebestruktur. Sie besteht aus funktionellen Einheiten, den Leberläppchen. Diese sind aus zwei ineinandergreifenden Netzwerken zusammengesetzt, den Sinusoiden für den Blutfluss sowie den Gallenkanälchen für die Gallensekretion und den Gallenfluss. Ein solcher Aufbau erschwert es, die dreidimensionale Organisation und die gesamte Gewebestruktur aus zweidimensionalen histologischen Bildern zu erkennen.
Räumliches Modell
Um diese diagnostischen Einschränkungen zu überwinden, hat das Forscherteam um Max-Planck-Direktor Marino Zerial gemeinsam mit Kollegen der Universitätskliniken Dresden, Rostock und Kiel sowie dem Zentrum für Informationsdienste und Hochleistungsrechnen an der Technischen Universität Dresden dreidimensionale und räumlich aufgelöste geometrische und funktionelle Modelle des menschlichen Lebergewebes in verschiedenen Stadien der Erkrankung entwickelt.
Bereits 2017 hatte die Forschungsgruppe von Marino Zerial durch eine umfassende 3D-Analyse der Gewebestruktur ein Modell des Gallenkanalnetzwerks und des Gallenflusses der Mausleber aufgebaut. Nun hat das Team die 3D-Organisation von menschlichem Lebergewebe untersucht. Obwohl in 2D-Bildern bereits einige Defekte zu erkennen sind, können die Veränderungen von Gallenkanälchen und Sinusoiden erst bei einer 3D-Rekonstruktion erkannt werden. Fabián Segovia-Miranda, der Erstautor der Studie, berichtet: „Dank Fortschritten in der Multi-Photonenmikroskopie sowie verbesserten Methoden, um die Transparenz von Gewebe zu erhöhen, können wir dickere Gewebeschnitte hochauflösend abbilden und damit räumliche Informationen gewinnen.“
Die digitale 3D-Rekonstruktion des Lebergewebes diente dann als Grundlage, um die Dynamik der Gallenflüssigkeit durch ein vom ZIH erstelltes Modell zu simulieren. „Während die Strömungsdynamik des Blutflusses durch die vergleichsweise großen Kapillaren bereits mittels Computersimulationen untersucht wurde, war dies für die Galle bisher unmöglich, da es an exakten geometrischen Daten des menschlichen Gewebes simultan über alle relevanten Skalen hinweg mangelte“, erklärt Lutz Brusch vom Zentrum für Informationsdienste und Hochleistungsrechnen.
Beeinträchtigter Gallenfluss
Durch die Kombination von digitaler Bildrekonstruktion und Computermodellierung konnten die Forscher eine Reihe von Zell- und Gewebeparametern identifizieren, die mit dem Fortschreiten der nicht-alkoholischen Fettlebererkrankung in Zusammenhang stehen. „Wir haben festgestellt, dass die Struktur des 3D-Gallenkanalnetzwerks im erkrankten Gewebe völlig anders ist. Solche strukturellen Veränderungen haben auch entscheidende funktionelle Auswirkungen. Durch eine personalisierte Simulation des Gallenflusses haben wir herausgefunden, dass der Gallenfluss in einigen kleinen Bereichen des Gewebes beeinträchtigt ist, was auch als Mikro-Cholestase bezeichnet wird“, sagt Segovia-Miranda.
Marino Zerial, der auch dem Zentrum für Systembiologie Dresden angehört, gibt einen Ausblick: „Die hochauflösende Medizin ebnet den Weg für die Diagnose von Krankheiten im Frühstadium, lange bevor Symptome auftreten. Sie hilft uns auch, molekulare krankheitsbedingte Mechanismen zu identifizieren, um neue Therapien zu entwickeln.“ Jochen Hampe vom Universitätsklinikum Dresden ergänzt: „Hier erlaubt uns die dreidimensionale Analyse des Lebergewebes völlig neue Einblicke in die Krankheitsmechanismen. So verstehen wir damit viel besser, wie beispielsweise der Gallenfluss und das Fortschreiten der Erkrankung zusammenhängen. Hier ergeben sich auch neue Ansätze für Therapien.“