Forschungsbericht 2011 - Max-Planck-Institut für Pflanzenzüchtungsforschung
Molekulare Grundlagen und Diagnostik komplexer Merkmale von Nutzpflanzen am Beispiel Kartoffel
Sieglinde, Nicola und Frühgold
Trotz ihres gemeinsamen, im Erbgut enthaltenen Bauplans unterscheiden sich die Individuen einer Art in vielen Eigenschaften mehr oder weniger voneinander. Diese Tatsache erscheint selbstverständlich, wenn wir uns selbst oder zum Beispiel unsere Haustiere betrachten, aber bei Kartoffeln? Festkochend oder mehlig, das ist eine der wenigen Fragen, die sich die meisten Menschen beim Einkauf dieses Grundnahrungsmittels stellen. Hobbygärtner wissen natürlich auch um so genannte frühe, mittlere oder späte Kartoffelsorten. Aber mit Ausnahme von Landwirten, Züchtern und anderen Fachleuten dürfte der Mehrzahl unbekannt sein, dass die "Beschreibende Sortenliste Kartoffeln" des Bundessortenamts etwa 200 verschiedene Sorten enthält, die in Deutschland zugelassen sind, und dass es weltweit mehr als 4500 Kartoffelsorten gibt. Wodurch unterscheiden sich Nicola, Charlotte, Granola, Frühgold, Erntestolz, Sieglinde, Eurostar und wie sie alle heißen?
Zunächst sind da der Ertrag zu nennen und alle Eigenschaften einer Kartoffelpflanze, die den Ertrag ermöglichen und sichern, wie Wüchsigkeit, Reifezeit, Widerstandsfähigkeit gegen Krankheiten, aber auch gegen Hitze, Kälte und Trockenheit. Nicht weniger wichtig sind die äußeren und inneren Werte der Knolle, wie Knollenform und –farbe, Augentiefe, Fleischfarbe, Kochqualität, Geschmack, der Gehalt an Stärke, die Farbe von Kartoffelchips und Pommes Frites sowie die Widerstandsfähigkeit gegen mechanische Beschädigung. Die meisten dieser Eigenschaften sind komplex, das heißt, sie werden durch mehrere Gene, deren genaue Zahl unbekannt ist, sowie durch Umweltfaktoren kontrolliert. Die Merkmalsvariation zwischen den Sorten beruht darauf, dass natürliche, während der Evolution durch Mutation entstandene DNA-Varianten dieser Gene (Allele) das Merkmal positiv oder negativ beeinflussen und die Sorten unterschiedliche Allele beziehungsweise Allelkombinationen in ihrem Genom tragen. Ziel der Sortenzüchtung ist es, durch Kreuzung geeigneter Eltern und Auslese unter deren Nachkommen möglichst viele positive Merkmalsallele zu kombinieren. Dies ist umso schwieriger, je mehr und je komplexer diese Merkmale sind. Die Auswahl von Eltern und Nachkommen erfolgt derzeit meist indirekt, das heißt aufgrund der Merkmale selbst und nicht aufgrund der Gene, die den Merkmalen zugrunde liegen. Eine direkte Diagnose von Gen-Varianten mit positivem oder negativem Merkmalseffekt könnte diesen Prozess beschleunigen, präzisieren und Allelkombinationen ermöglichen, die ohne Gen-Diagnostik unauffindbar sind - oder mit anderen Worten: Man könnte Präzisionszüchtung betreiben. Voraussetzungen für die Gen-Diagnostik in der Pflanzenzüchtung sind (1) die Kenntnis der Genomregionen, in denen die entsprechenden Gene liegen, (2) die Kenntnis der molekularen Identität dieser Gene und (3) die Kenntnis der Gen-Varianten und ihre Wirkung auf ein bestimmtes Merkmal. Ziel der Arbeitsgruppe am Institut ist es, wesentliche Grundlagen für eine Gen-Diagnostik in der Kartoffelzüchtung zur Verfügung zu stellen.
Assoziationskartierung
Analog zur Humangenetik führt der Weg zur Gen-Diagnostik bei der Kartoffel über die Assoziationskartierung. Eine Population von genetisch verschiedenen Individuen wird einerseits quantitativ auf ein Merkmal und andererseits auf DNA-Variation hin untersucht. Für Letzteres gibt es zwei Vorgehensweisen. Entweder werden gezielt Kandidatengene auf DNA-Variation untersucht, das heißt Gene, von denen bekannt ist oder vermutet wird, dass sie eine Funktion bei der Ausprägung des Merkmals haben. Oder aber das ganze Genom wird systematisch auf DNA-Variation hin überprüft (whole genome association = WGA). Bei der Kartoffel basierten die ersten Assoziationsstudien auf Kandidatengenen, weil die komplette Sequenz des Kartoffelgenoms, die für WGA erforderlich wäre, nicht zur Verfügung stand. Beiden Vorgehensweisen gemeinsam ist, dass alle aufgespürten DNA-Varianten mit statistischen Methoden darauf geprüft werden, ob sie mit besseren oder schlechteren Werten eines Merkmals korrelieren - also mit diesem assoziiert sind.
In Zusammenarbeit mit Kartoffelzüchtern wurden am Institut erste Assoziationsstudien für komplexe Merkmale der Kartoffel durchgeführt. Dabei wurden hoch signifikante Assoziationen zwischen Kandidatengenen und den Merkmalen gefunden. Im Folgenden werden zwei Beispiele zusammengefasst.
Die Kraut- und Knollenfäule: Eine weltweit gefürchtete Kartoffelkrankheit
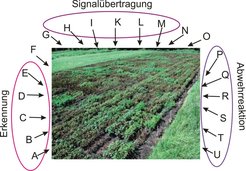
Die Kraut- und Knollenfäule wird durch den Oomyzeten Phytophthora infestans verursacht. Sie ist die weltweit wichtigste Kartoffelkrankheit, deren Bekämpfung mit Fungiziden der größte Kostenfaktor im Kartoffelanbau ist. Eine Population von etwa 190 verschiedenen Kartoffel-Zuchtklonen wurde über zwei Jahre im Feld auf Resistenz gegen P. infestans geprüft (Abb. 1). Die Population zeigte eine quantitative Variation der Krautfäuleresistenz. Die gleichen Individuen wurden für single nucleotide polymorphisms (SNPs) an Kandidaten-Genorten (Loci) genotypisiert. Kandidatengene für Krautfäuleresistenz sind solche, die an der Erkennung eines Pathogens, der Signalübertragung oder der Abwehrreaktion beteiligt sind. Die SNPs wurden auf Assoziation mit Krautfäuleresistenz getestet, das heißt es wurde geprüft, ob die Häufigkeit eines SNP-Allels signifikant mit dem Resistenzniveau ansteigt oder abnimmt. Es wurden mehrere Assoziationen mit Kandidatengenen gefunden, darunter eine hoch signifikante Assoziation mit dem Gen StAOS2 [1]. StAOS2 kodiert eine Allene-Oxide-Synthase, ein Enzym des Jasmonsäure-Biosynthesewegs. Jasmonsäure, ihre Vorstufen und Derivate sind Pflanzenhormone mit vielfältigen Wirkungen. Unter anderem spielen sie eine Rolle in der Signalübertragung bei der Pathogenabwehr. Die funktionelle Analyse von StAOS2-Allelen in einer aos Defektmutante der Modellpflanze Arabidopsis thaliana zeigte, dass StAOS2-Allele sehr wahrscheinlich kausal an der Variation von Krautfäuleresistenz beteiligt sind [2].
Schwarzfleckigkeit und Proteomanalysen

Wie Äpfel und Birnen bekommen auch Kartoffeln schwarzbraune Druckstellen unter der Schale, wenn man sie mechanisch beschädigt- die eine Sorte mehr, die andere weniger (Abb. 2). Die Neigung einer Sorte zur Schwarzfleckigkeit ist ein wichtiges Qualitätsmerkmal, da Kartoffeln bei Ernte und Transport nicht in Watte gebettet werden. Die Auswahl von Kandidatengenen fällt hier schwer, da sehr unterschiedliche Prozesse eine Rolle spielen, die aber biochemisch und molekularbiologisch kaum untersucht sind. Daher wurde bei diesen Untersuchungen eine Analyse des Knollen-Proteoms mit einer Assoziationskartierung kombiniert. Die Knollen-Proteinmuster von Sorten mit starker oder geringer Neigung zur Schwarzfleckigkeit wurden miteinander verglichen. Qualitativ oder quantitativ unterschiedliche Proteine wurden massenspektrometrisch identifiziert und nachfolgend die sie kodierenden Gene bestimmt. Darunter befanden sich bekannte Kandidatengene wie Polyphenoloxidasen - das sind Enzyme, die die Bildung der braunschwarzen Pigmente katalysieren - aber auch eine Lipase, also ein Enzym, das Triglyceride spaltet - letzteres war bisher nicht mit dem Merkmal Schwarzfleckigkeit in Verbindung gebracht worden [3]. Eine Population von etwa 200 Sorten und Zuchtklonen, deren Neigung zur Schwarzfleckigkeit quantifiziert worden war, wurde dann in Hinblick auf DNA-Variation in bekannten und neuen Kandidatengenen, resultierend aus der Proteomanalyse, genotypisiert. Auch hier konnten mehrere, möglicherweise kausale Assoziationen von Allelen der Kandidatengene mit dem Merkmal "Schwarzfleckigkeit" identifiziert werden [4].
Künftige Arbeiten werden sich mit whole genome association beschäftigen sowie mit der strukturellen und funktionellen Analyse von Allelen der Kandidatengene, die mit komplexen Merkmalen der Kartoffel assoziiert sind.

